利用 metaphlan2 结果计算 alpha 多样性利用 metaphlan2 结果计算 alpha 多样性前期回顾 结果展示 格式转化 什么是 α 多样性 什么是 Shannon 指数 Shannon 指数如何计算 前期回顾MetaPhlAn2 是分析微生物群落(细菌、古菌、真核生物和病毒)组成的工具,可以基于宏基因组数据,获得微生物群体中种水平精度的组成,包括细菌、古菌、真核生物和病毒
如果有株水平基因组的物种,也可以追踪和研究
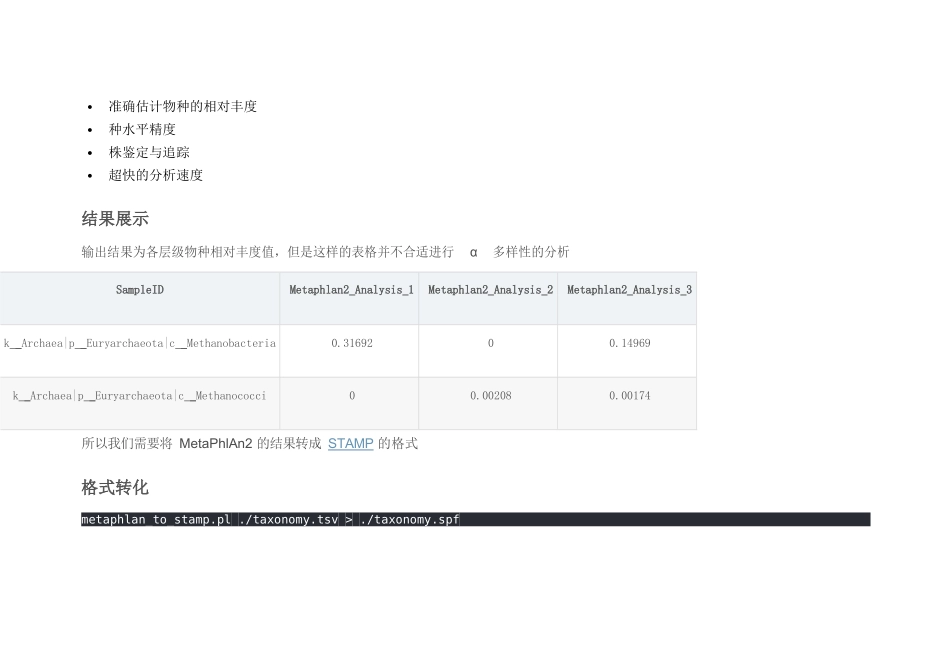
MetaPhlAn2 整理了超过 17000 个参考基因组,包括 13500 个细菌和古菌,3500 个病毒和 110 种真核生物,汇编整理了 100 万+类群特异的标记基因,可以实现:精确的分类群分配准确估计物种的相对丰度种水平精度株鉴定与追踪超快的分析速度结果展示输出结果为各层级物种相对丰度值,但是这样的表格并不合适进行 α 多样性的分析SampleID Metaphlan2_Analysis_1 Metaphlan2_Analysis_2 Metaphlan2_Analysis_3 k Archaea|p Euryarchaeota|c Methanobacteria 0
31692 0 0
14969 k Archaea|p Euryarchaeota|c Methanococci 0 0
00208 0
00174 所以我们需要将 MetaPhlAn2 的结果转成 STAMP 的格式格式转化metaphlan_to_stamp
/taxonomy
/taxonomy
spf1以上程序可以在 https://github
com/LangilleLab/microbiome_helper 上下载到因为去掉了重复的分层注释,所以 STAMP 结果是Kingdom Phylum Class M