Arlequin3
1 的使用说明Arlequin 功能的概述Molecular diversity—分子多态性Mismatch distribution—错配分布Haplotype frequency estimation—单倍型频率估计Linkage disequilibrium —连锁不平衡: 检测不同位点上等位基因的非随机关联Hardy-Weinberg equilibrium—哈温—伯格平衡Tajima’s neutrality test— Tajima 中性检测Fu’ s neutrality test— Fu 中性检测Ewens-watterson neutrality test— Ewens-watterson中性检测以上三个中性检测都是基于无限位点模型,适用于DNA sequence和 RFLP 单倍型
Chakraboety’s amalgamation test— Chakraboety’s 融合检测,检测人群的均一性和同质性,和中性选择等
Minimu Spanning Network(MSN ,最小扩张树或称之为最小支撑树,给予分子差异
AMOV A—分子差异度分析,用以评测人群的遗传结构Parwise genetic distances—遗传距离的估计Exact test of population differentiation—检测随机交配群体单倍型的非随机分布Assignment test of genotype—通过估计等位基因平率将单个基因型分被盗特定的人群中
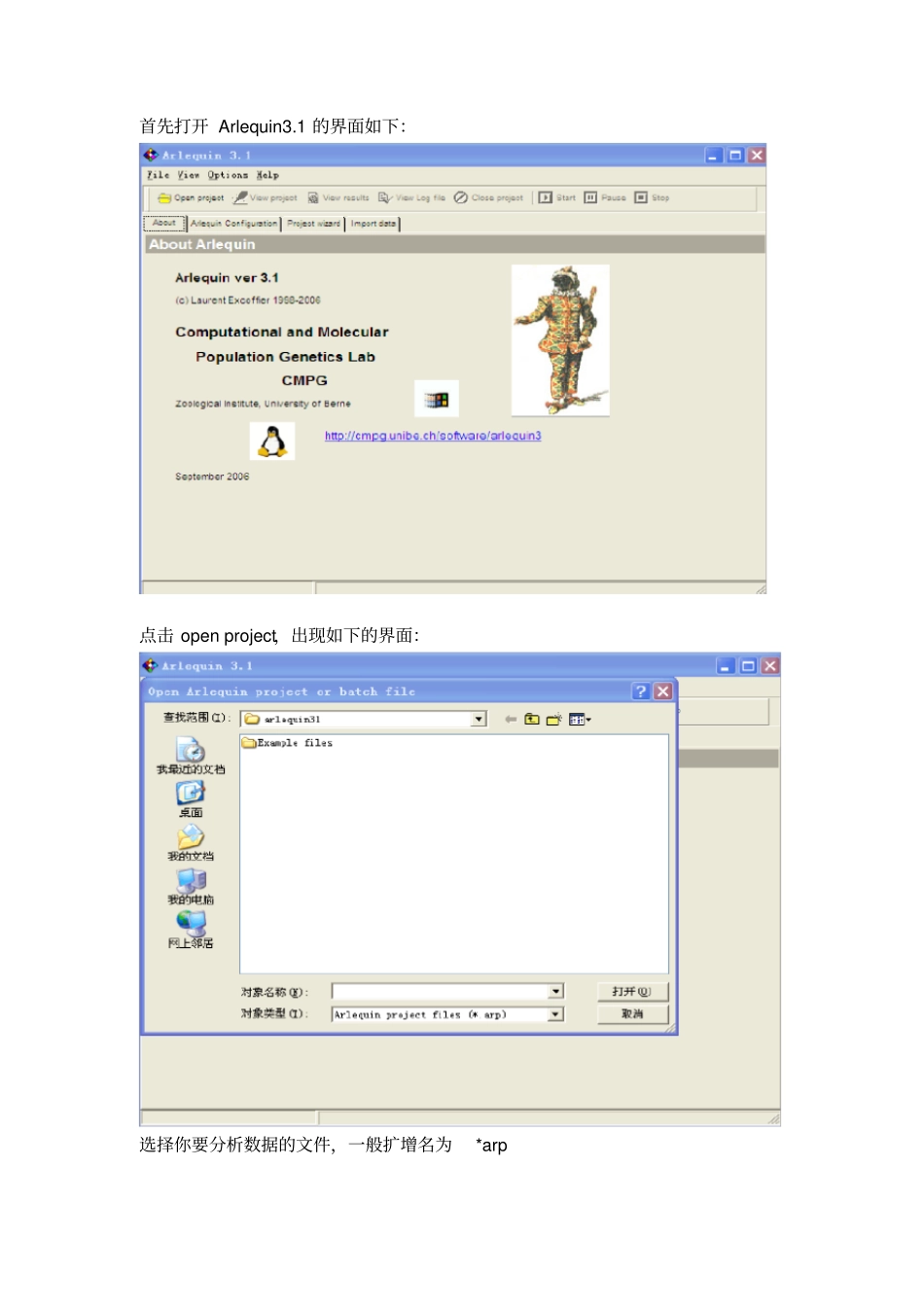
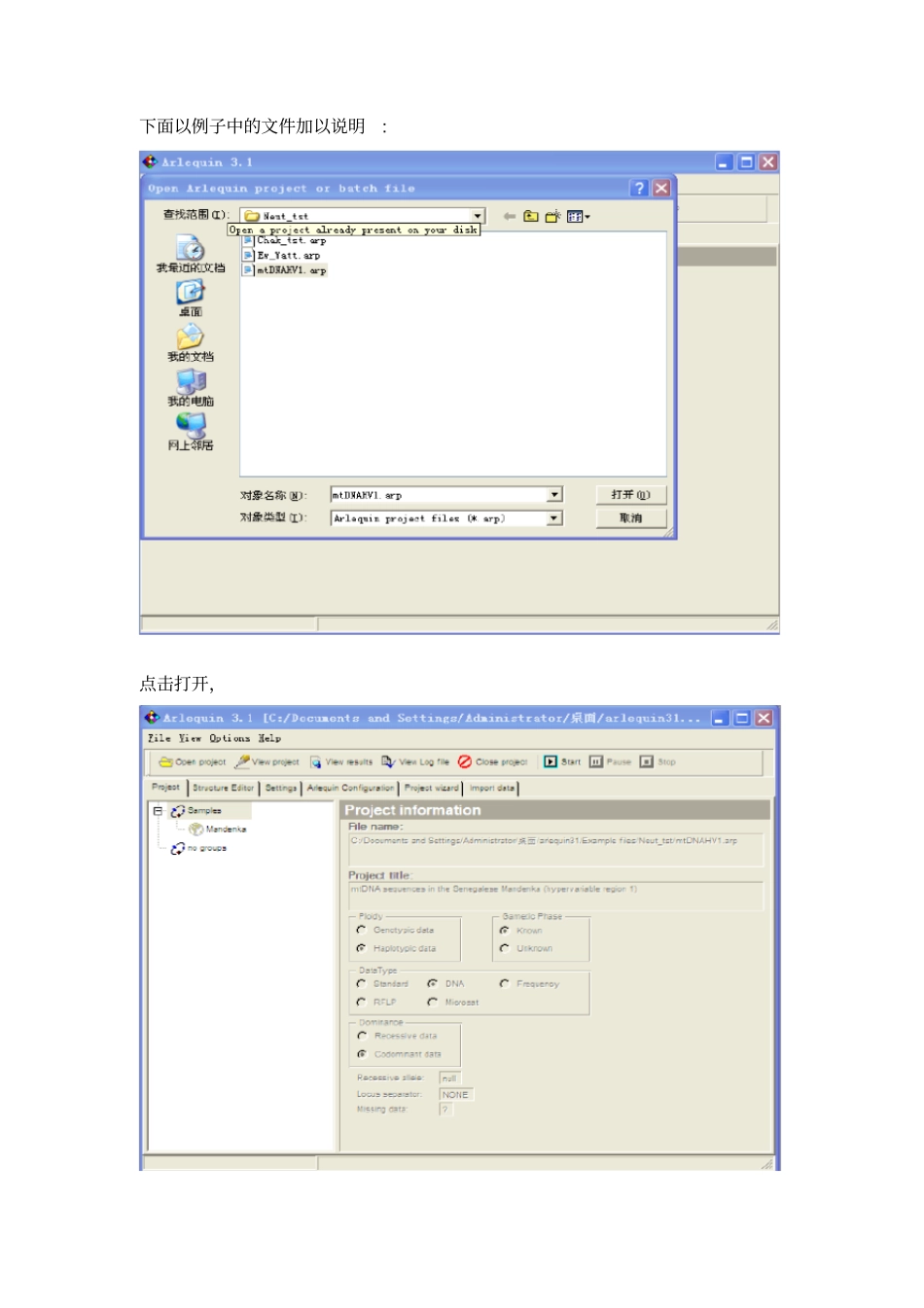
Arlequin3
1 分析的数据文件的格式必须是以*arq 为扩增名方法:用 Clustalx 比对后保存一个 PHY 格式的文件,在 DNAsp 中打开该文件,点击 Generate中的 Haplotype date file ,设置 considered,其余的参数不变,